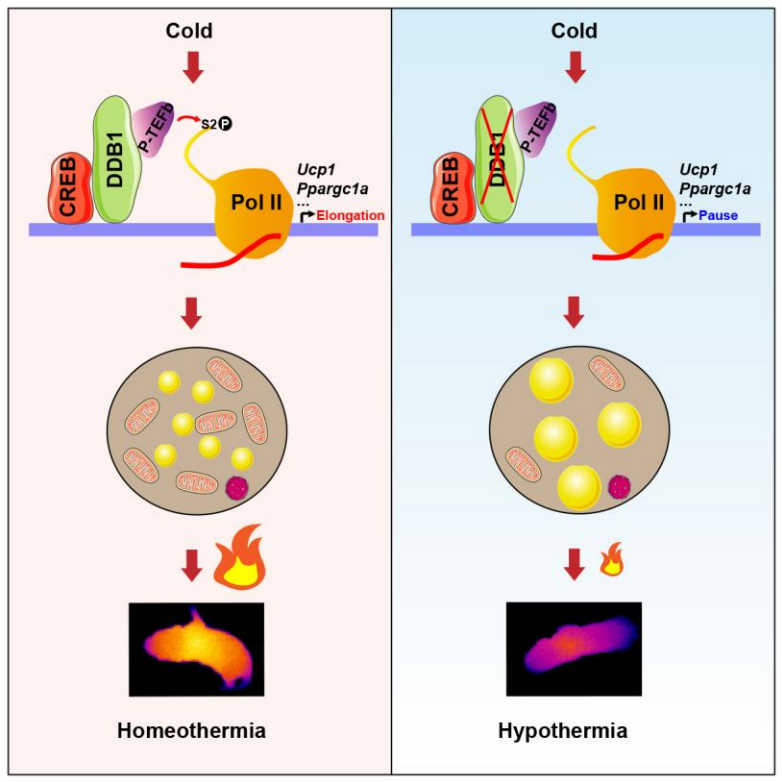
农学院张国平团队联合多家单位解析小麦族盐生植物海大麦的基因组与耐盐机制
2022年5月4日,浙江大学作物科学研究所张国平教授团队与湖南农业大学吴德志教授等合作在plant Communications上在线发表了题为The genome and gene editing system of sea barleygrass provide a novel platform for cereal domestication and stress tolerance studies的研究论文(https://doi.org/10.1016/j.xplc.2022.100333)解析了小麦族盐生植物海大麦的参考基因组和耐盐机制,并构建了该物种的高效基因编辑体系。
小麦族是禾本科重要的粮食作物来源,包括小麦、大麦和黑麦等麦类作物,全球年产量高达9亿吨,占总谷物产量的30%。海大麦(Hordeum marinum Huds., 2n = 2x = 14, XaXa) 是大、小麦的野生近缘种,属于盐生植物,具有耐盐、耐渍等优异特性,且与普通小麦有一定的可交配性,可为作物抗逆遗传改良提供优异基因资源。目前,由于缺乏基因组信息及有效的遗传转化体系,海大麦的相关研究及其育种利用进展缓慢。
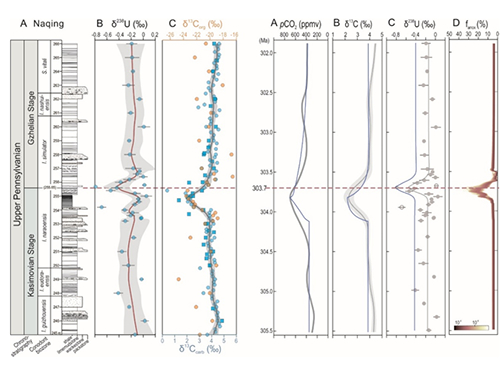
浙江大学张国平教授团队联合湖南农业大学、诺禾致源生物科技公司等单位历时五年完成了海大麦参考基因组组装及高效基因编辑体系构建。利用pacBio SMRT、Illumina pE、10×Genomics和Hi-C技术组装了一个3,816 Mb的染色体水平基因组,Contig和Super-scaffold N50值分别为6.83 Mb和524.47 Mb,96.8% (3.69 Gb) 的序列被定位到7条染色体上。在全基因组序列中注释得到41,405个高置信度基因,BUSCO完整性指数为98.4%; LTR组装指数(LAI)为12.7,属于参考基因组级别(图1)。
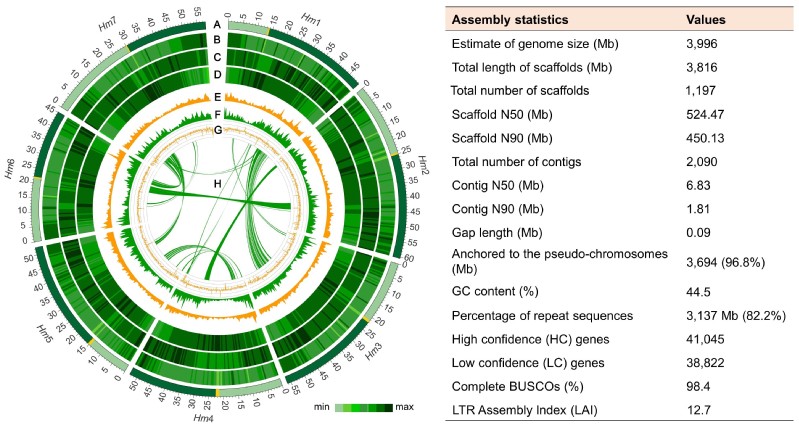
图1 海大麦基因组特征
在组装基因组的基础上,构建了海大麦的高效转化体系和基因编辑体系,遗传转化效率为28.7%;将HmSOS1的特异靶位点克隆至pUB-Cas9-TaU6-sgRNA载体利用上述体系进行转化,两次独立试验的转基因幼苗的靶点突变效率均为100%;海大麦sos1突变体表现盐敏感表型,其根部对Na+的吸收量显著高于野生型,揭示了HmSOS1基因调控海大麦耐盐性的重要作用(图2)。海大麦参考基因组信息和高效基因编辑体系对小麦族作物抗逆机制与育种改良研究均具有重要参考价值。
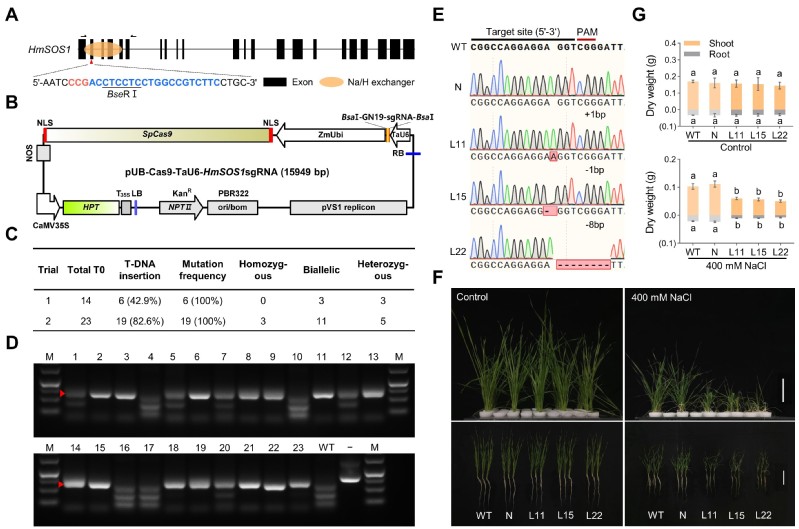
图2 基于CRISpR/Cas9的海大麦高效基因编辑体系
本研究由浙江大学、湖南农业大学和诺禾致源生物科技公司等多家单位协作完成。浙江大学作物科学研究所邝刘辉博士生、沈秋芳副研究员、叶玲珍副研究员和诺禾致源公司陈力杨为该论文共同第一作者,浙江大学张国平教授和湖南农业大学吴德志教授为共同通讯作者,西悉尼大学陈仲华教授和英国James Hutton研究所Robbie Waugh教授等也参与了该研究工作。研究受国家重点研发计划项目(2018YFD1000704)、国家自然科学基金(32071934)和现代农业产业技术体系等项目资助。目前,海大麦基因组序列已上传至国家基因组科学数据中心(NGDC,pRJCA009391),欢迎广大同行下载使用。
文章链接:https://www.cell.com/plant-communications/fulltext/S2590-3462(22)00083-9