基因组“无用”序列稳定染色质三维结构及细胞稳态机制
人类基因组中的非编码序列在多种生物学过程中发挥着至关重要的作用,如非编码RNA、启动子、增强子和转座子等。作为在基因组中占比约98%的非编码区域,仍有大量是功能未知的,这些曾被认为是基因组中“垃圾”的区域,已被逐渐证实存在重要功能。基因组的三维结构会影响基因的转录调控或其他细胞生命活动,然而,除了研究较多的增强子-启动子成环所形成的三维结构在调控基因表达上的作用外,其他大量非编码序列在形成和维持正确三维染色质结构上是否具有潜在功能,在目前的研究中是被忽视的一个方向。之前有研究表明,改变非编码序列能够改变染色质结构,如切除一些拓扑结构相关结构域(TAD)的边界序列能够导致异常的基因表达,诱发疾病产生。除了TAD边界序列这一特殊类型,非编码序列在结构上的重要性目前还没有系统性的研究,尤其是一些与TAD无关、无任何表观遗传信号或功能元件注释的区域。
2021年11月3日,加州大学圣地亚哥分校(UCSD)王巍课题组与北京大学、生命科学联合中心魏文胜课题组在Science Advances上联合发表了题为Noncoding loci without epigenomic signals can be essential for maintaining global chromatin organization and cell viability的研究论文,该研究基于分析得到的能够形成大量三维互作的非编码区域hub,通过CRISpR/Cas9系统对非编码hub位点进行靶向片段删除进而进行高通量功能性筛选,发现了一些不包含任何表观遗传标记的位点能够显著影响细胞生长和存活,并对于稳定全局染色质结构至关重要。
该研究基于来源于7个人类正常细胞系和癌细胞系中的5-kb分辨率的Hi-C数据(Raoet al.Cell2014),将其中显著的染色体内互作对整合为片段互作网络,发现了其中与维持染色体三维结构至关重要的互作中心位点hub。这些位点聚集于异染色质区域,染色质开放性较低,且与已注释位点(包括蛋白编码基因和非编码RNA等)重合性较少(图1A-B)。为了探究hub位点是否对于稳定染色质结构具有重要作用,该研究基于实验室建立的CRISpR/Cas9系统介导的pgRNA片段删除策略(Zhuet al.Nature Biotechnology2016),在K562细胞中对其中960个非编码hub位点进行高通量功能性筛选,发现了35个影响细胞存活或增殖的重要功能区(图1C)。其中,hub_22_7(chr22: 17,325,000-17,330,000, hg19)位点的切除能够在K562细胞系中导致显著的细胞死亡或细胞生长抑制,而不影响其他多种癌细胞(图1D)。
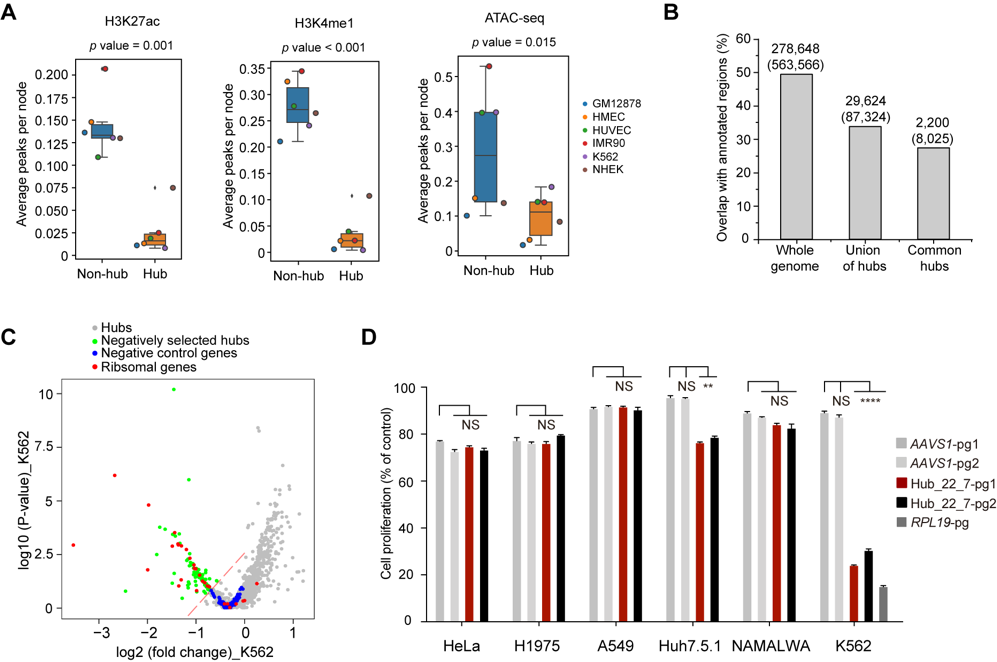
图1 hub位点的发现及高通量功能性筛选
筛选得到的hub位点不与任何蛋白编码基因、非编码RNA和TAD有重叠,其中77.1%(27/35)无任何组蛋白修饰或转录因子结合位点,包括hub_22_7位点(图2A)。相比于切除基因组安全位点AAVS1,Hi-C分析表明该位点的切除会在多个染色体上产生大范围染色质结构的变化。单细胞测序进一步发现,该hub位点的切除会激活一系列细胞凋亡相关基因的表达,改变同一染色体上远端区域多个与细胞存活相关基因如THOC5的表达,结合Hi-C数据发现其增强子与启动子的互作发生破坏(图2B-D)。由此表明,hub位点的破坏所诱导产生的染色质结构改变能够影响远端基因的转录调控,进而影响细胞功能。该研究首次揭示了无任何表观遗传信号的非编码位点能够稳定染色质三维结构并维持细胞存活,通过对这类hub位点的发现、筛选与功能解析,将进一步丰富对基因组非编码区域的功能阐述以及揭示其在维持三维基因组结构中的重要作用。
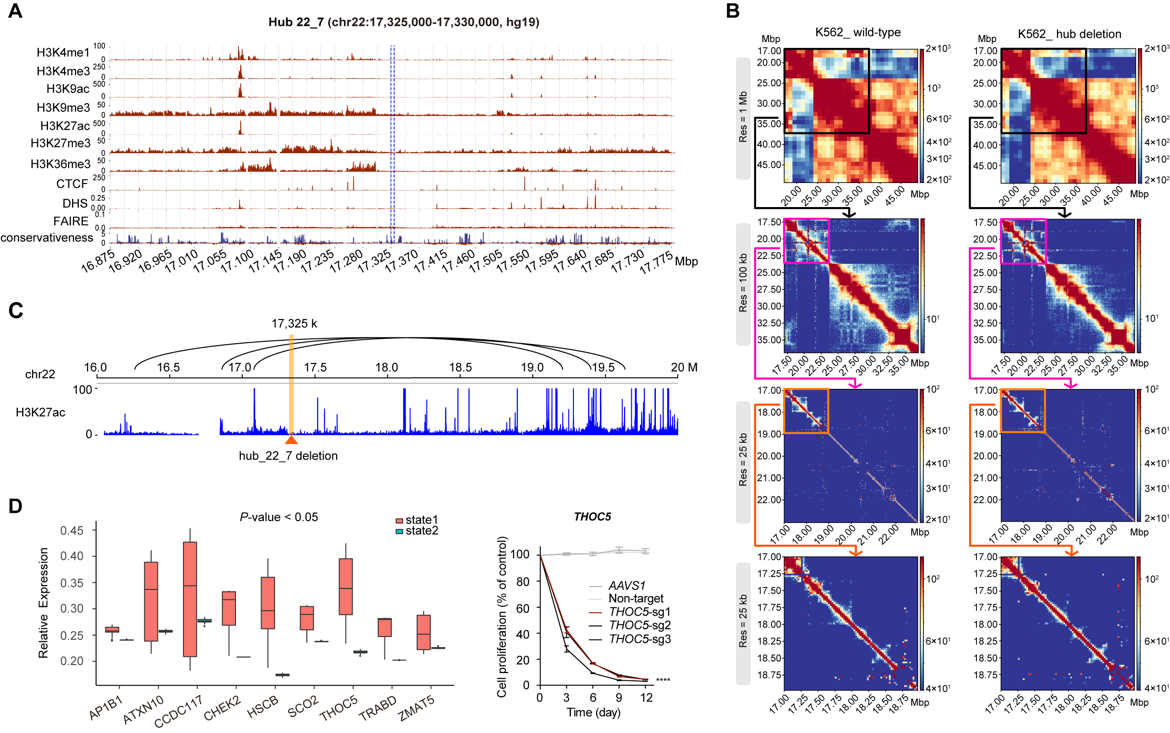
图2 hub位点切除导致染色质三维结构和基因表达的同时改变
加州大学圣地亚哥分校丁博博士,北京大学刘莹博士、刘志恒博士和UCSD博士生郑丽娜为该论文的共同第一作者,加州大学圣地亚哥分校王巍教授和北京大学魏文胜教授为论文共同通讯作者。该研究项目得到了加州再生医学研究所(CIRM)、美国国立卫生研究院(NIH)、国家自然科学基金、北京市科委生命科学前沿创新培育项目、北京未来基因诊断高精尖创新中心、生命科学联合中心以及中国博士后科学基金的支持。
原文链接:https://www.science.org/doi/10.1126/sciadv.abi6020






























